میکروبیوتای مرتبط با تومور جزء مهمی از ریزمحیط تومور (TME) در 33 نوع سرطان انسانی است. با این حال، شواهد کمی در مورد توزیع فضایی و محلی سازی این میکروب ها در سلول های تومور در دسترس است.
پرداختن به این شکاف در تحقیقات، اخیرا طبیعت مطالعه مجله برهمکنشهای فضایی، سلولی و مولکولی میکروب میزبان-میکروب را در سرطان سلول سنگفرشی دهان (OSCC) و سرطان کولورکتال (CRC) ارزیابی کرد. در این مطالعه، دانشمندان برهمکنشهای سلولی میزبان-باکتری، فضایی و مولکولی را در TME با استفاده از توالییابی RNA تک سلولی (scRNA-seq) و در موقعیت فن آوری های فضایی پروفایل
مطالعه: تأثیر میکروبیوتای داخل توموری بر ناهمگونی فضایی و سلولی در سرطان. اعتبار تصویر: jovan vitanovski / Shutterstock
زمینه
به طور معمول، تومورهای بیماران سرطانی شامل سلول های بدخیم است که توسط شبکه ای ترکیبی از سلول های غیر بدخیم احاطه شده اند. این سلول ها ممکن است بر اساس فراوانی و نوع خود، اثرات جانبی یا ضد تومورزا از خود نشان دهند. هر دو درونکشتگاهی و in vivo آزمایشها وجود باکتریها را در میکروبیوتای مرتبط با تومور نشان دادهاند که نقش مهمی در توسعه سرطان، نظارت بر ایمنی، متاستاز و مقاومت شیمیایی دارند. تجزیه و تحلیل مولکولی و داده های تصویربرداری زیستی نیز وجود میکروبیوتای داخل توموری را در انواع عمده سرطان نشان داده است.
شواهدی در مورد هویت خاص سلولهای میزبان که از طریق آن میکروبهای مرتبط با تومور با سلولهای تومور بیماران سرطانی تعامل دارند، وجود ندارد. علاوه بر این، شواهد کمی در ارتباط با شناسایی سلول های خاصی که ارگانیسم ها را در خود جای داده اند، مستند شده است. اثر تعاملات سلولی میزبان میکروبی دقیق و توزیع فضایی میکروبیوتای داخل توموری بر قابلیتهای عملکردی آنها در TME آشکار نیست.
درباره مطالعه
توالی یابی ژن 16S rRNA بافت های تومور بیماران CRC نشان دهنده وجود باکتری های مختلف از جمله فوزوباکتریوم. فراوانی این باکتری در بیماران CRC متفاوت است. تجزیه و تحلیل دندروگرام و تجزیه و تحلیل مؤلفههای اصلی با خوشهبندی تنوع بتا نشان داد که اکثر بیماران سرطانی ترکیبات میکروبیوم نسبتاً پایداری داشتند. با این وجود، اکثر بیماران درجات مختلفی از ناهمگنی را در ترکیب میکروبیوم داخل توموری نشان دادند.
RNAscope – فلورسانس در موقعیت هیبریداسیون (RNAscope-FISH) تصویربرداری توزیع فضایی ناهمگن جوامع باکتریایی در TME را تایید کرد. داده های مبتنی بر RNAscope-FISH وجود فوزوباکتریوم هستهکه بیشتر از طریق تجزیه و تحلیل میکروبیوم و روش کمی PCR تایید شد.
10 x Visium spatial transcriptomics نیز برای شناسایی و تجزیه و تحلیل توزیع فضایی میکروبیوتای داخل توموری نمونههای CRC و OSCC استفاده شد. این رویکرد 28 درصد از نقاط ضبط شده را در تومورهای OSCC و 46 درصد از تومورهای CRC را شناسایی کرد.
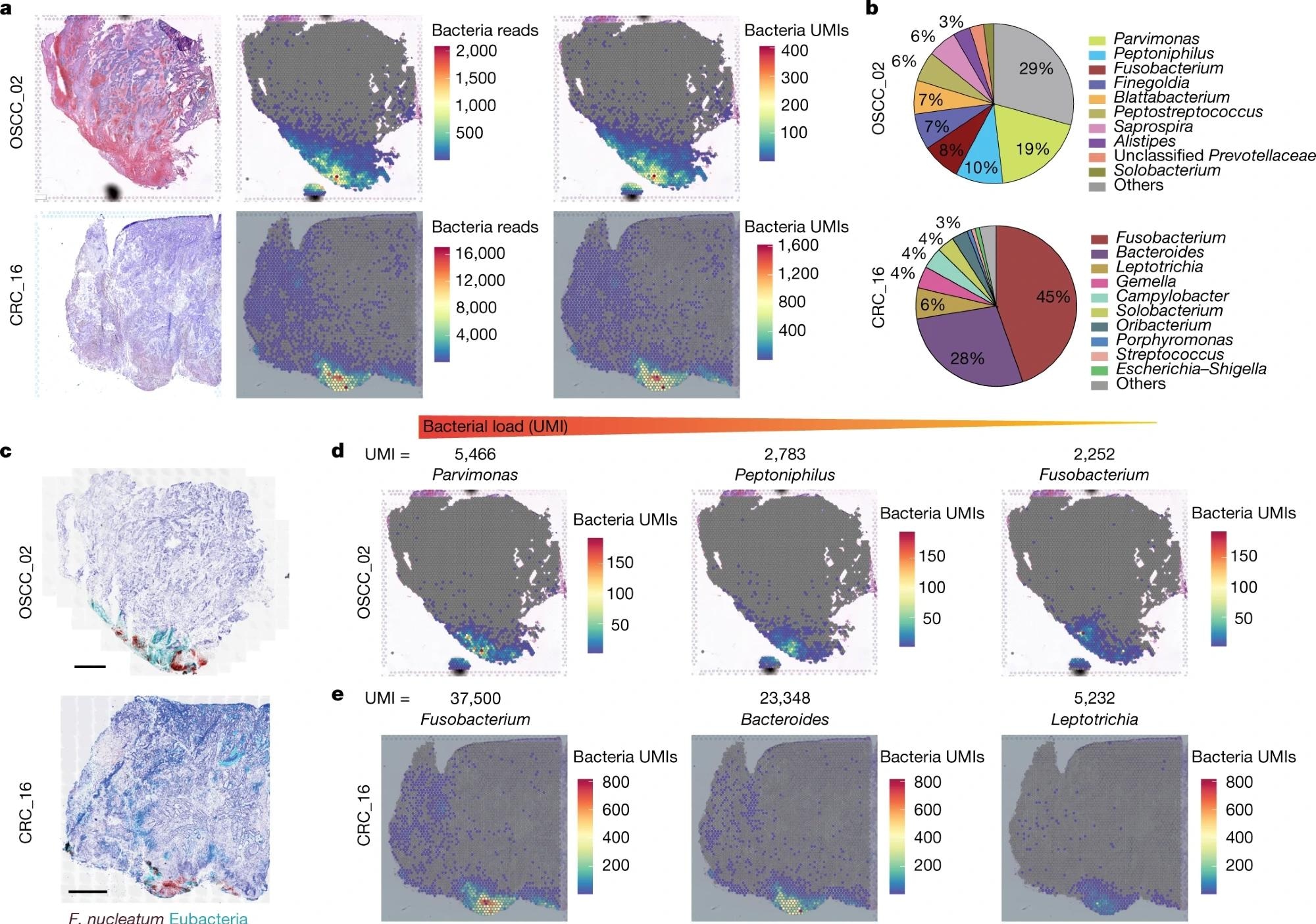 آرنگآمیزی هماتوکسیلین و ائوزین (H&E) (سمت چپ)، توزیع فضایی کل کل باکتریها (مرکز) و رونوشتهای UMI کل (راست) در سراسر بافت تومور در اسلایدهای 10x Visium از نمونههای OSCC و CRC انسانی. بنمودار دایره ای از 10 جنس باکتریایی برتر که در داده های توالی یابی RNA 10x Visium از تومورهای OSCC و CRC شناسایی شده اند. جتصویربرداری RNAscope-FISH که توزیع باکتری ها را در سراسر بافت تومور در یک اسلاید متوالی به دنبال بخش 10x Visium نشان می دهد. پروب F. nucleatum قرمز و پروب اوباکتری فیروزه ای است. میله های مقیاس، 1 میلی متر. دتوزیع فضایی UMI های Parvimonas، Peptoniphilus و Fusobacterium در داده های نمونه OSCC 10x Visium شناسایی شد. هتوزیع فضایی Fusobacterium، Bacteroides و Leptotrichia UMIs در دادههای نمونه 10x Visium CRC شناسایی شد.
آرنگآمیزی هماتوکسیلین و ائوزین (H&E) (سمت چپ)، توزیع فضایی کل کل باکتریها (مرکز) و رونوشتهای UMI کل (راست) در سراسر بافت تومور در اسلایدهای 10x Visium از نمونههای OSCC و CRC انسانی. بنمودار دایره ای از 10 جنس باکتریایی برتر که در داده های توالی یابی RNA 10x Visium از تومورهای OSCC و CRC شناسایی شده اند. جتصویربرداری RNAscope-FISH که توزیع باکتری ها را در سراسر بافت تومور در یک اسلاید متوالی به دنبال بخش 10x Visium نشان می دهد. پروب F. nucleatum قرمز و پروب اوباکتری فیروزه ای است. میله های مقیاس، 1 میلی متر. دتوزیع فضایی UMI های Parvimonas، Peptoniphilus و Fusobacterium در داده های نمونه OSCC 10x Visium شناسایی شد. هتوزیع فضایی Fusobacterium، Bacteroides و Leptotrichia UMIs در دادههای نمونه 10x Visium CRC شناسایی شد.
در تومور OSCC، پرویموناس، پپتونیفیلوس، و فوزوباکتریوم در حالی که سویه های غالب بودند فوزوباکتریوم و باکتریوئیدها جنس های غالب در تومور CRC بودند.
تکنیک رونویسی فضایی 10x Visium امکان تشخیص مستقیم، کمی سازی و نقشه برداری فضایی باکتری های زنده در بافت های دست نخورده تومور بیماران سرطانی را فراهم کرد. همچنین پیچیدگی تعاملات میکروبیوتای داخل توموری را در بافتهای تومور نشان داد.
پلت فرم پروفایل فضایی دیجیتال GeoMx (DSP) به تعیین کمیت نمایه بیان ۷۷ پروتئین مرتبط با پیشرفت سرطان و ایمنی ضد تومور کمک کرد. این تکنیک، همراه با RNAscope و رویکرد ایمونوهیستوشیمی (IHC)، نشان داد که جوامع باکتریایی دارای میکرونیچهای بسیار سرکوبکننده ایمنی هستند و چندان عروقی نیستند. علاوه بر این، سویه های باکتریایی مستعد سکونت در سلول های بدخیم با سطوح کاهش یافته Ki-67 هستند.
تکنیک INVADEseq (توالییابی بیان مبتنی بر چسبندگی) برای ارزیابی تعامل سلول به سلول باکتری-میزبان در TME و تأثیر بر رونویسی سلول میزبان توسعه داده شد. این تکنیک با معرفی یک پرایمر برای هدف قرار دادن مناطق حفاظت شده 16S rRNA باکتریایی همراه است. متعاقباً، میتوان کتابخانههای cDNA با رونوشتهای باکتریایی از سلولهای انسانی مرتبط با باکتری تولید کرد. یکی از جنبه های حیاتی این روش این است که معرفی پرایمر بر پروفایل بیان ژن سلول های CRC انسانی تأثیر نمی گذارد.
تکنیک INVADEseq با استفاده از رده سلولی CRC انسانی HCT116 که به گونههای باکتریایی آلوده شده بود، تأیید شد، اف. هسته، پورفیروموناس لثه ای، و Prevotella intermedia. این نقشه برداری از جمعیت باکتری ها را در سلول های منفرد انسان امکان پذیر کرد. نکته مهم این است که INVADEseq نقش آن را تایید کرد اف. هسته و پ. لثه در تأثیرگذاری بر ناهمگنی سلول های سرطانی این سویههای باکتریایی برنامههای رونویسی متمایز را تغییر میدهند که به خوشهبندی سلولی خاص کمک میکنند. تغییر مسیرهای رونویسی نیز با بروز التهاب، خواب سلولی، متاستاز و ترمیم DNA همراه است.
نتیجه گیری
مطالعه حاضر نشان داد که سلولهای سرطانی آلوده به باکتری، محیط اطراف خود را به عنوان یک سلول منفرد تحت تأثیر قرار میدهند، که متعاقباً سلولهای میلوئیدی را در قلمرو باکتری به کار میگیرند. مشخص شد که میکروبیوم درون تومور یک پدیده تصادفی نیست. در عوض، بیان شد که حضور باکتری در یک تومور یک فرآیند بسیار سازمان یافته در میکرونیچ ها با عملکردهای ایمنی و سلول های اپیتلیال است که بر پیشرفت سرطان تأثیر می گذارد.
حتی اگر مطالعه حاضر بر دو نوع سرطان متمرکز بود، ابزارها و تکنیکها میتوانند برای مطالعه همه انواع سرطانهای اصلی و آنهایی که حاوی میکروبیوتای داخل توموری هستند مورد استفاده قرار گیرند.
